
近日,大连理工大学环境学院常洋洋副教授等在化学领域著名学术期刊Angewandte Chemie International Edition上发表了题为“Deep Learning–Enhanced DNAzyme-Driven Rolling-Circle Amplification Encoding for Multibacterial Detection”的研究论文。该研究针对食源性致病菌快速、精准、高通量检测需求,创新性地构建了一种DNAzyme驱动的滚环扩增/分子信标编码系统(DRM-ES),结合基于智能手机成像的卷积神经网络(CNN)深度学习,实现了对大批量样本中多重致病菌的同步识别与精准定量。
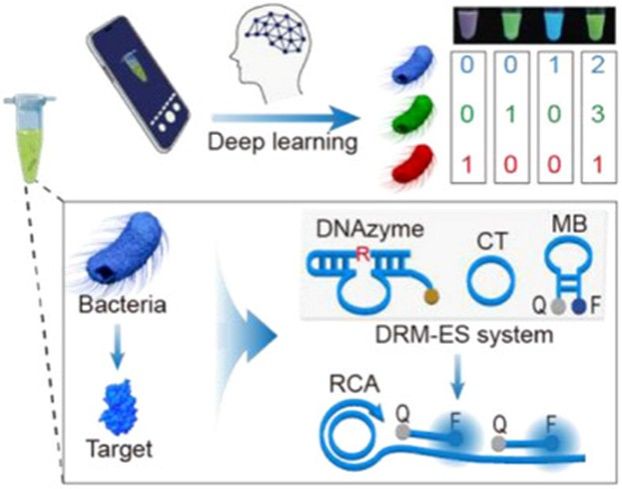
该工作取得了如下突破:
活菌特异性识别:利用由活菌分泌特定蛋白激活的脱氧核酶(DNAzyme)作为识别元件,有效规避了死菌干扰,实现了对致病菌风险的精准评估。
信号放大与颜色编码:经切割后的DNAzyme片段可有效触发滚环扩增(RCA)反应,产生大量串联重复序列,可特异性识别并开启蓝、绿、红三色分子信标,将不同细菌识别事件转化为肉眼可辨、仪器可量化的荧光指纹图谱。
深度学习智能解码:基于2800张荧光图像构建并训练卷积神经网络模型,可对智能手机采集的复杂混合荧光信号实现自动化解析,直接输出细菌种类与精确浓度而无需人工判读。
该方法在食品、临床及环境样本中均表现出优异检测性能:对金黄色葡萄球菌、椰毒假单胞菌、大肠杆菌的检测灵敏度分别低至10²、10¹、10¹ CFU/mL;以传统培养法为金标准对照,阳性符合率为100%,阴性符合率不低于95.2%。在32个样本阵列的并行检测中,成功鉴定出29份自然污染样本,具备良好的高通量筛查潜力。此外,本方法无需依赖大型实验室仪器,可为食品安全现场监管、临床感染即时诊断及环境病原微生物大规模筛查,提供一种高灵敏、可区分死活菌、支持多重检测的便携式通用检测平台。
本研究得到了国家重点研发计划(2023YFB3208200)、国家自然科学基金(22425602、22406015)、辽宁省博士科研启动基金(2025-BS-0071、2025-BS-0022)、大连市科技人才创新支持计划(2024RJ001、2023R0008)以及中央高校基本科研业务费专项资金(DUT25RC(3)033)的支持。
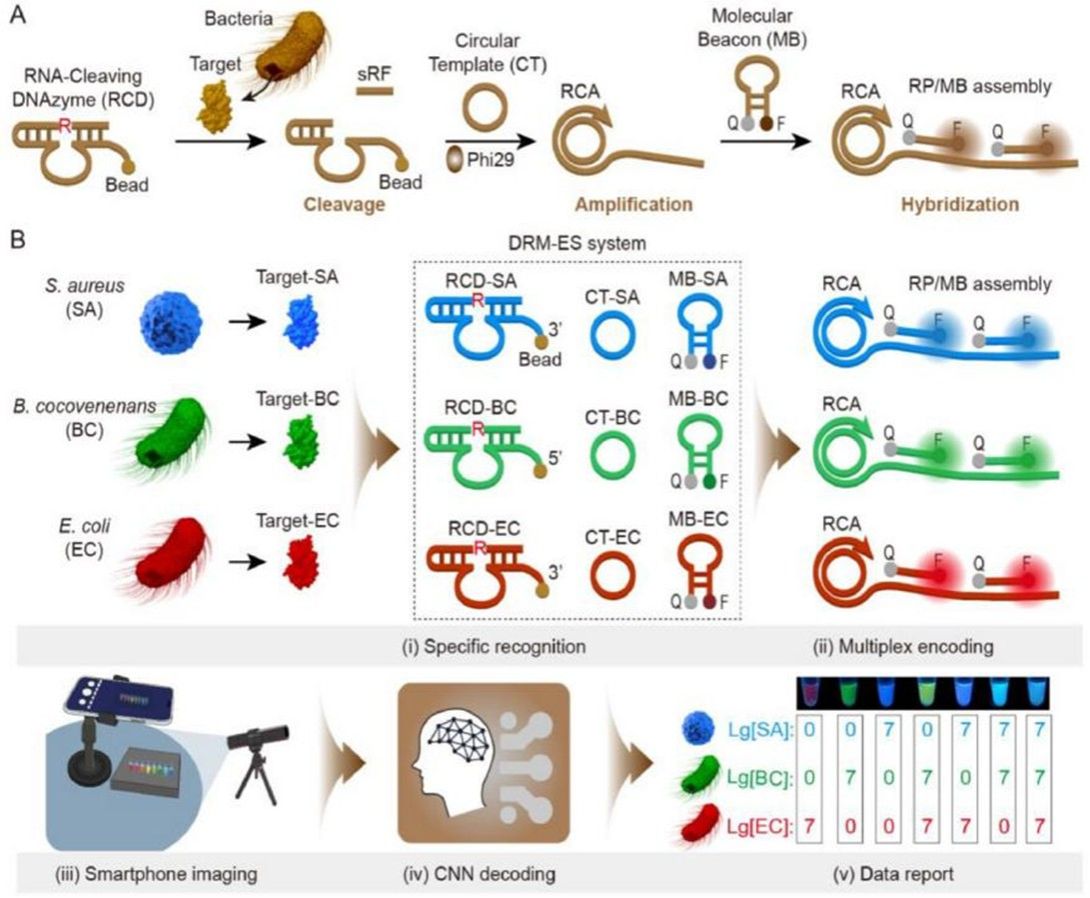
图1. 深度学习辅助DRM-ES系统用于多重活菌检测原理示意图
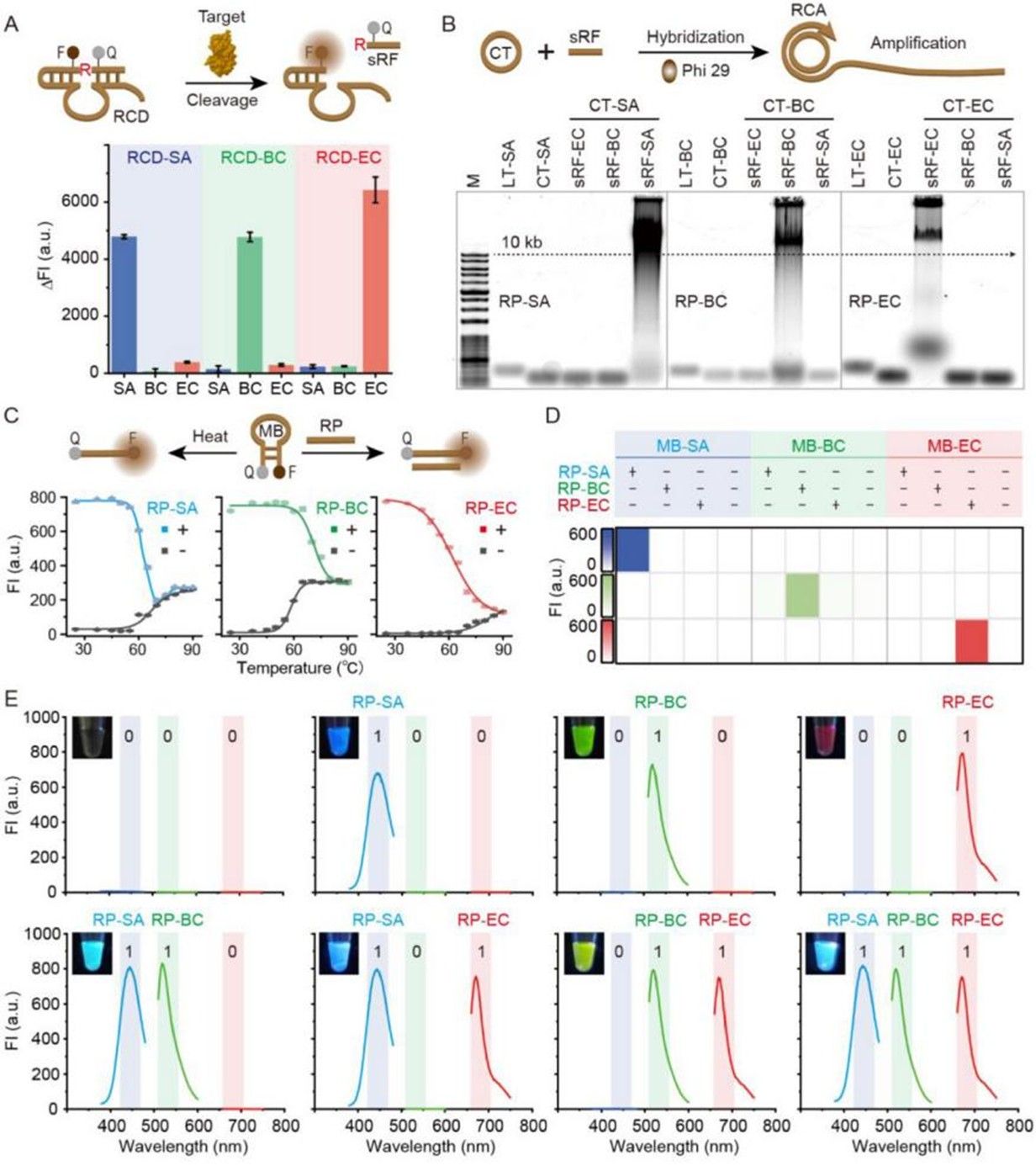
图2. DRM-ES的组装及可行性验证
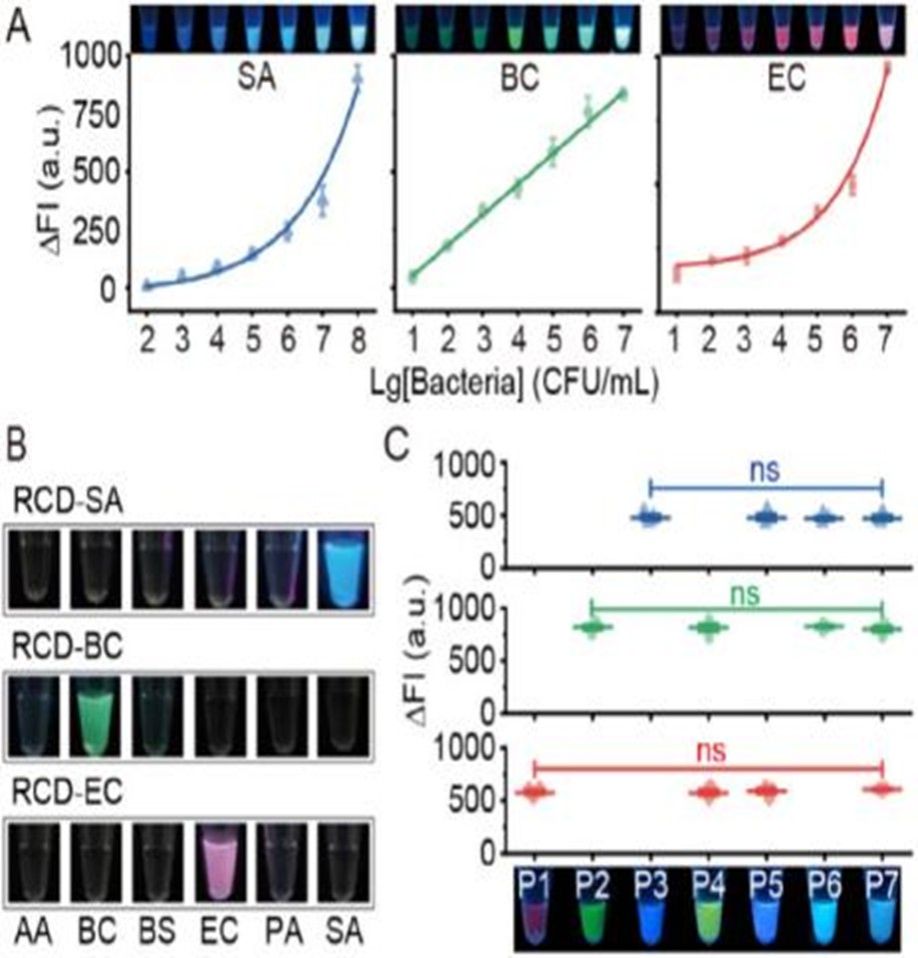
图3. DRM-ES的分析性能评估
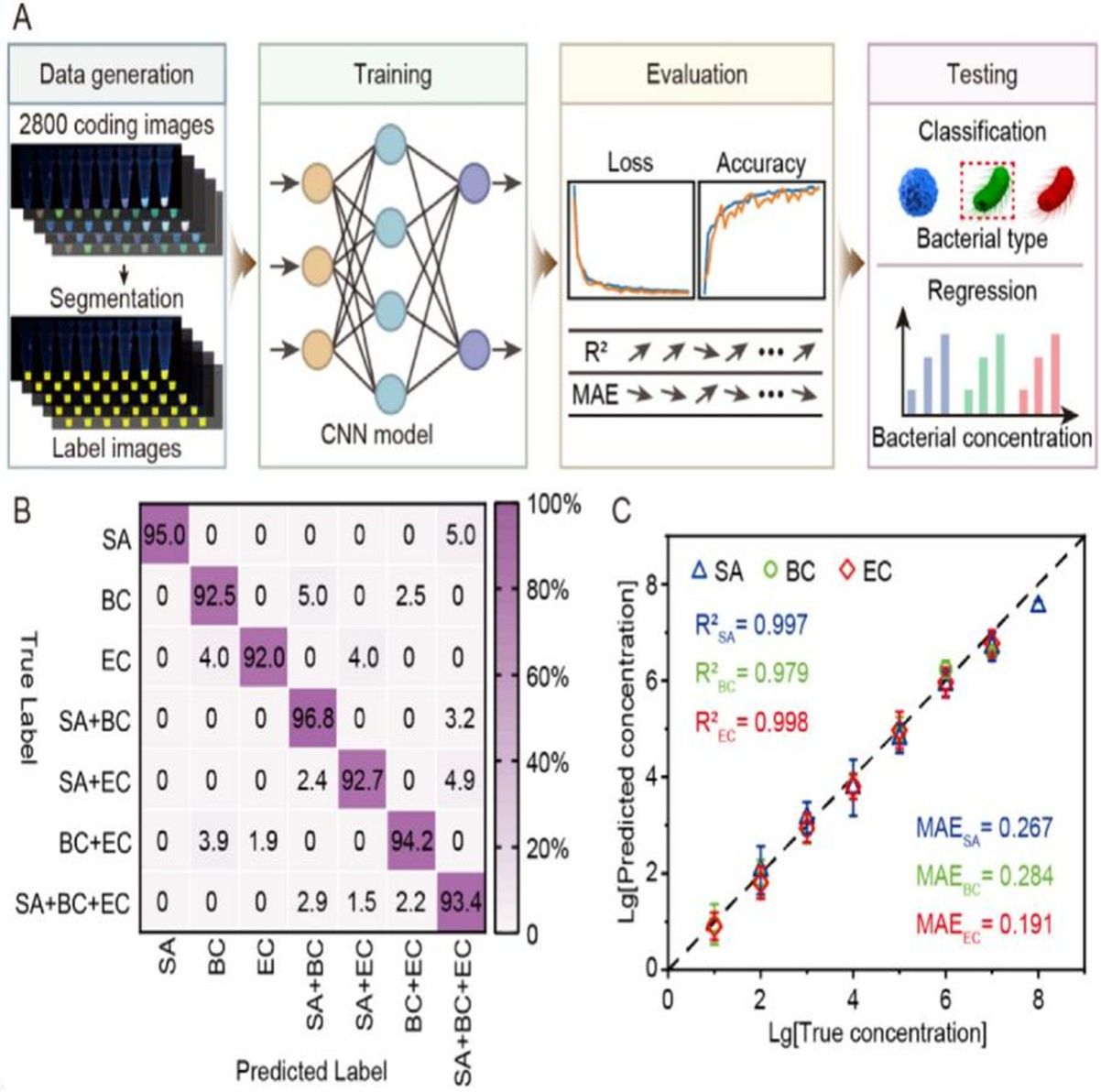
图4. 基于深度学习的DRM-ES图像量化分析
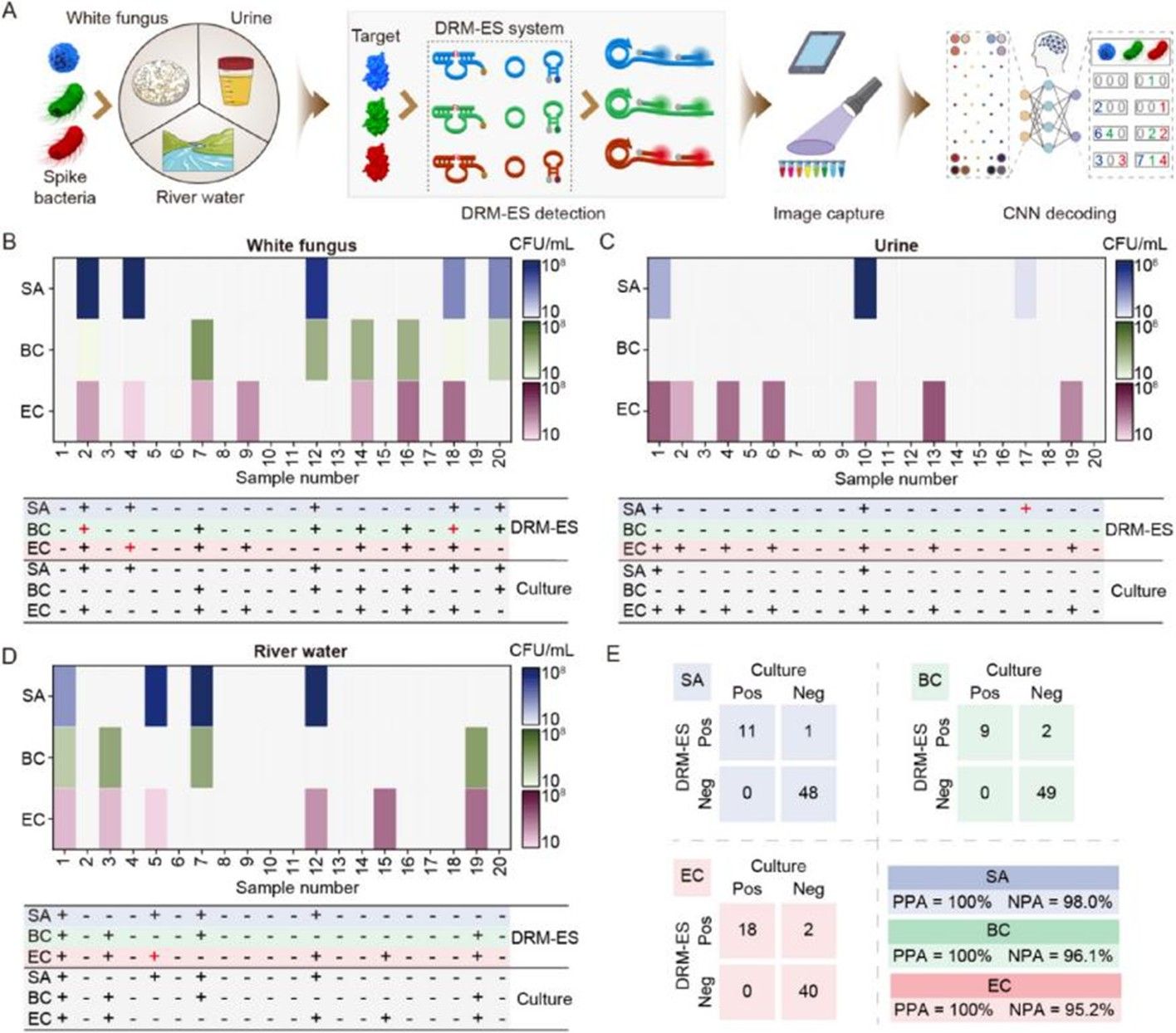
图5. DRM-ES在实际基质中的即时检测验证
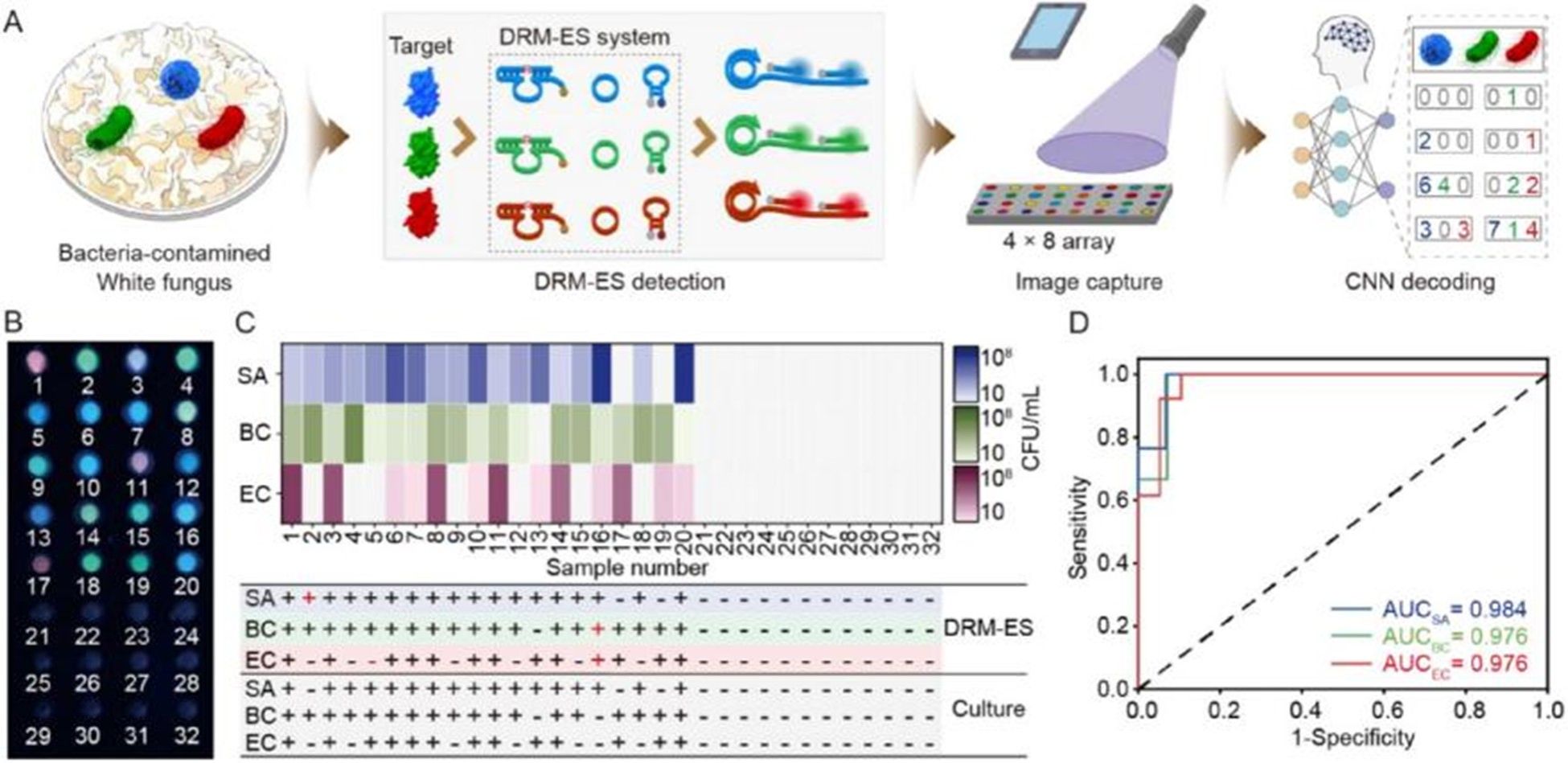
图6. DRM-ES对受污染样品阵列式筛查分析
文章信息:
原文链接:https://doi.org/10.1002/anie.4446117